
2021-05-20
今天结合nature medicine中的一篇文章,和大家分享下热图的绘制,主要亮点功能是:
(1)名称太多看不清,如何只展示特定的名称?
(2)数据太密集,如何快速调整单元格的宽和高?
论文页面:

文章链接:https://www.nature.com/articles/s41591-020-0944-y
代码及数据:https://github.com/ajwilk/2020_Wilk_COVID
拟复现图片样式:Fig2中的热图样式
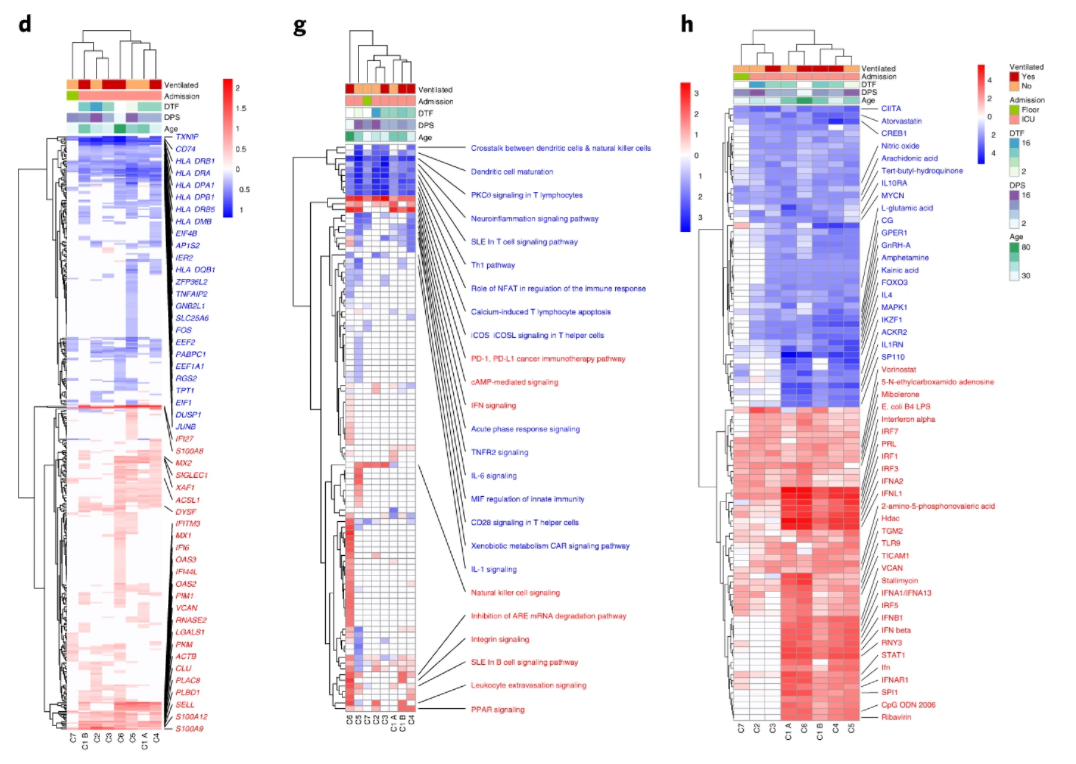
图1 拟复现图片样式
使用数据:数据大家可以通过上述链接下载,附件是一个rds文件(1.5G,一般电脑慎加载会卡死的), 我们已经下载处理好了一个示例数据(如图2所示)。大家可以通过基因云(https://www.genescloud.cn)的云端文件进行选择使用, 具体可参考下图7 云端数据选择
name | C1A | C1B | C2 | C3 | C4 | C5 | C6 | C7 |
ACKR2 | -3.606 | -2.4 | 0 | 0 | -3.273 | -3.701 | -3.701 | 0 |
amphetamine | -2.491 | -2.491 | -1.944 | -2.303 | -2.491 | -2.664 | -2.094 | 0 |
anisomycin | -2.218 | -2.218 | -1.243 | -2.218 | -2.218 | -2.433 | -1.074 | -0.506 |
APEX1 | -2.236 | -2.236 | 0 | -2 | -2.236 | -2.236 | -2 | 0 |
arachidonic acid | -2.403 | -2.063 | -1.679 | -1.806 | -2.19 | -2.19 | -0.993 | -1.894 |
atorvastatin | -2.967 | -3.13 | -2.236 | -1.569 | -3.13 | -2.828 | -1.906 | -2 |
bicuculline | -2.942 | -2.469 | -0.728 | -1.107 | -2.469 | -1.709 | -0.397 | 0 |
bucladesine | -1.792 | -1.611 | -0.733 | -1.392 | -2.718 | -2.385 | -1.239 | -0.179 |
图2 示例数据
按照惯例,我们先画一个基本的热图。
library(pheatmap) library(grid) mat <- read.delim("heatmap.txt",sep="\t",row.names=1) pheatmap(mat)
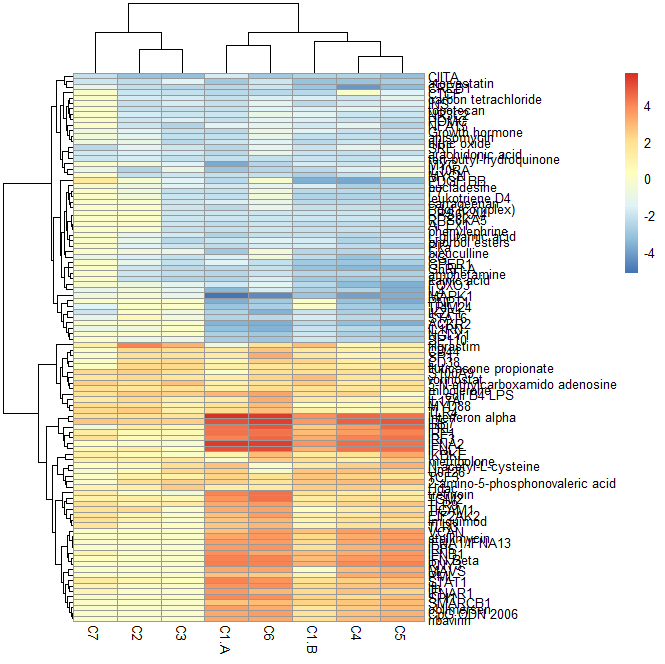
图3 初始热图
上图样式不是很好看,存在以下几点需要完善:①颜色不是很好看,且有灰色边框线条;②行名有很多重叠无法识别;③ 热图缺少分组信息, 接下来我们通过代码继续完善。
# 设置颜色 color <- c("blue", "white", "red") myColor <- colorRampPalette(color)(100) # 添加分组信息 annotation_col <- data.frame(Group = factor(rep(c("T", "C"),4))) rownames(annotation_col) <- colnames(mat) # 绘制热图 p1 <- pheatmap(mat,color = myColor, border_color=NA, annotation_col = annotation_col)
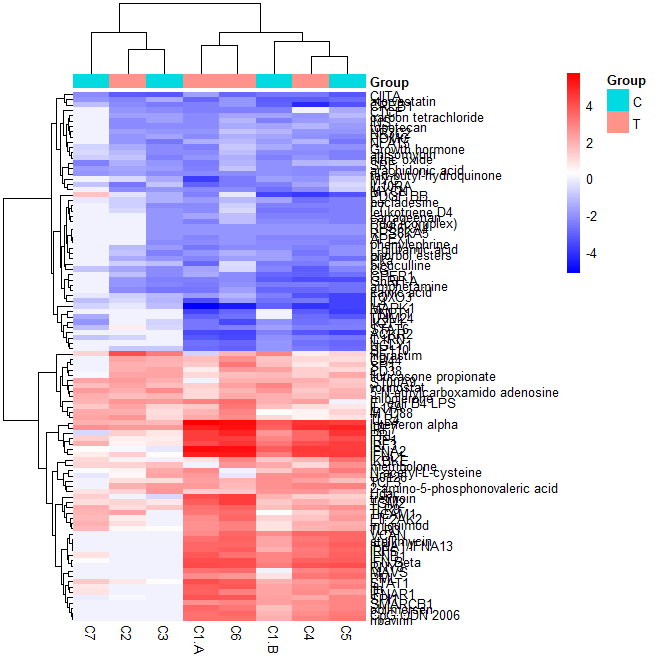
图4 美化后热图一
接下来通过调整单元格高度,使得文字错开。
# 调整单元格高度,避免文字重叠 p1 <- pheatmap(mat,color = myColor, border_color=NA, annotation_col = annotation_col, cellheight=10)
图5 美化后热图二
上图通过调整单元格高度调整,文字是清晰可分辨了,但是图片的整体高度会被拉长,放在文章里面不太方便查看。那么我们是否可以只展示特定的行名呢? 首先我们来看下文中提及的,可以实现只展示特定行名的函数:
# 展示特定行名函数 add.flag <- function(pheatmap, kept.labels, repel.degree) { heatmap <- pheatmap$gtable new.label <- heatmap$grobs[[which(heatmap$layout$name == "row_names")]] # keep only labels in kept.labels, replace the rest with "" new.label$label <- ifelse(new.label$label %in% kept.labels, new.label$label, "") # calculate evenly spaced out y-axis positions repelled.y <- function(d, d.select, k = repel.degree){ # d = vector of distances for labels # d.select = vector of T/F for which labels are significant # recursive function to get current label positions # (note the unit is "npc" for all components of each distance) strip.npc <- function(dd){ if(!"unit.arithmetic" %in% class(dd)) { return(as.numeric(dd)) } d1 <- strip.npc(dd$arg1) d2 <- strip.npc(dd$arg2) fn <- dd$fname return(lazyeval::lazy_eval(paste(d1, fn, d2))) } full.range <- sapply(seq_along(d), function(i) strip.npc(d[i])) selected.range <- sapply(seq_along(d[d.select]), function(i) strip.npc(d[d.select][i])) return(unit(seq(from = max(selected.range) + k*(max(full.range) - max(selected.range)), to = min(selected.range) - k*(min(selected.range) - min(full.range)), length.out = sum(d.select)), "npc")) } new.y.positions <- repelled.y(new.label$y, d.select = new.label$label != "") new.flag <- segmentsGrob(x0 = new.label$x, x1 = new.label$x + unit(0.15, "npc"), y0 = new.label$y[new.label$label != ""], y1 = new.y.positions) # shift position for selected labels new.label$x <- new.label$x + unit(0.2, "npc") new.label$y[new.label$label != ""] <- new.y.positions # add flag to heatmap heatmap <- gtable::gtable_add_grob(x = heatmap, grobs = new.flag, t = 4, l = 4 ) # replace label positions in heatmap heatmap$grobs[[which(heatmap$layout$name == "row_names")]] <- new.label # plot result grid.newpage() grid.draw(heatmap) # return a copy of the heatmap invisibly invisible(heatmap) }
函数写好了,接下来我们看看具体效果。本示例随机抽取20个行名,添加到原来的热图中。具提代码如下,最终效果图如图6所示。
# 这里随机抽取20个基因进行展示
gene_name<-sample(rownames(mat),20)
add.flag(p1,kept.labels = gene_name,repel.degree = 0.2)
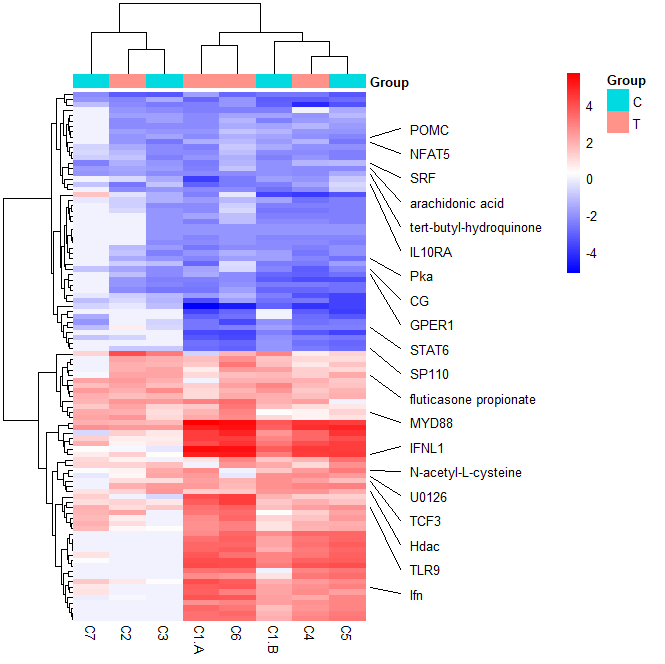
图6 美化后热图三
到此我们就成功的通过代码实现了一幅含有分组信息,只展示特定行名的热图,那么如何不通过代码实现呢?接下来,给大家分享下基因云(https://www.genescloud.cn)的“交互热图”,帮助你“0”代码快速制作漂亮的上述图表,同时还提供多种样式的在线调整。
为了方便大家学习实践,基因云平台已整合该文章数据,进入“交互热图”绘图页面,直接通过【文件上传→云端文件→公共数据】按照路径: Home>ref_data>COVID-19_data>交互热图,即可选择使用。
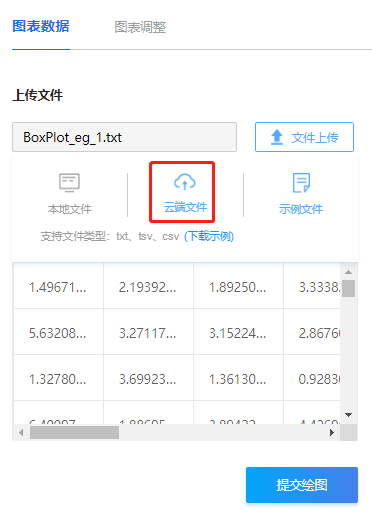
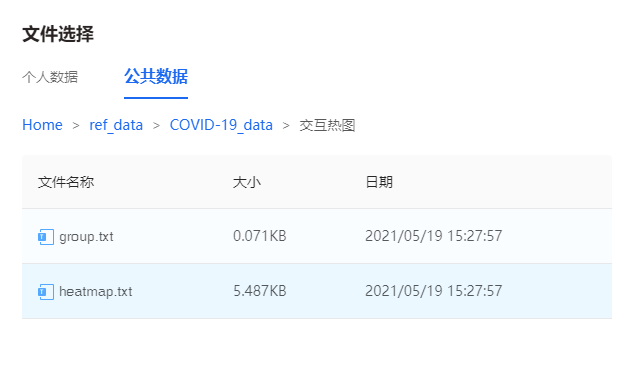
图7 云端数据选择
选择好数据和分组文件后,一键提交绘图。

图8 快速提交页面
(1)显示特定基因名称:在图表调整里面,选择【显示名称→行/行列】,下方会出现所有行名列表,可随意勾选你想要展示的名称。
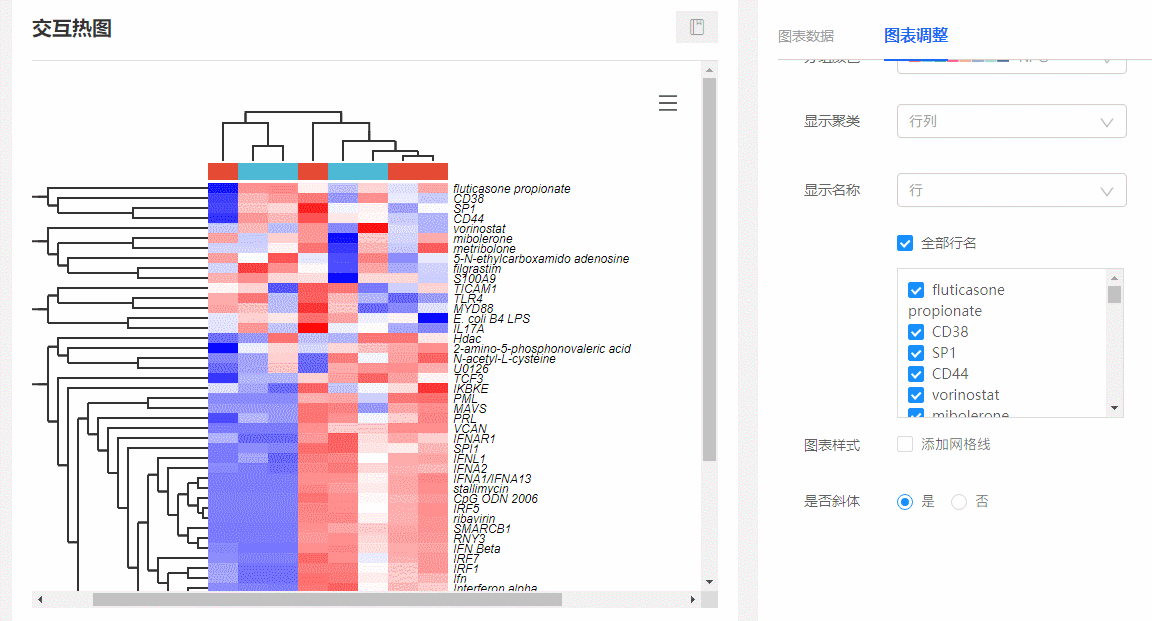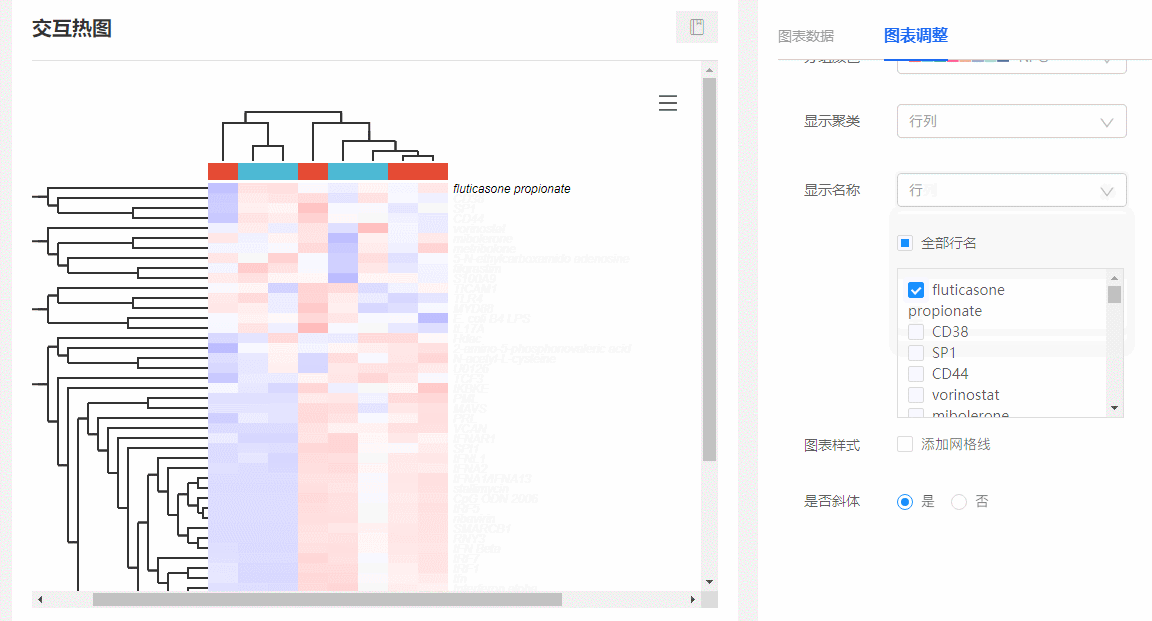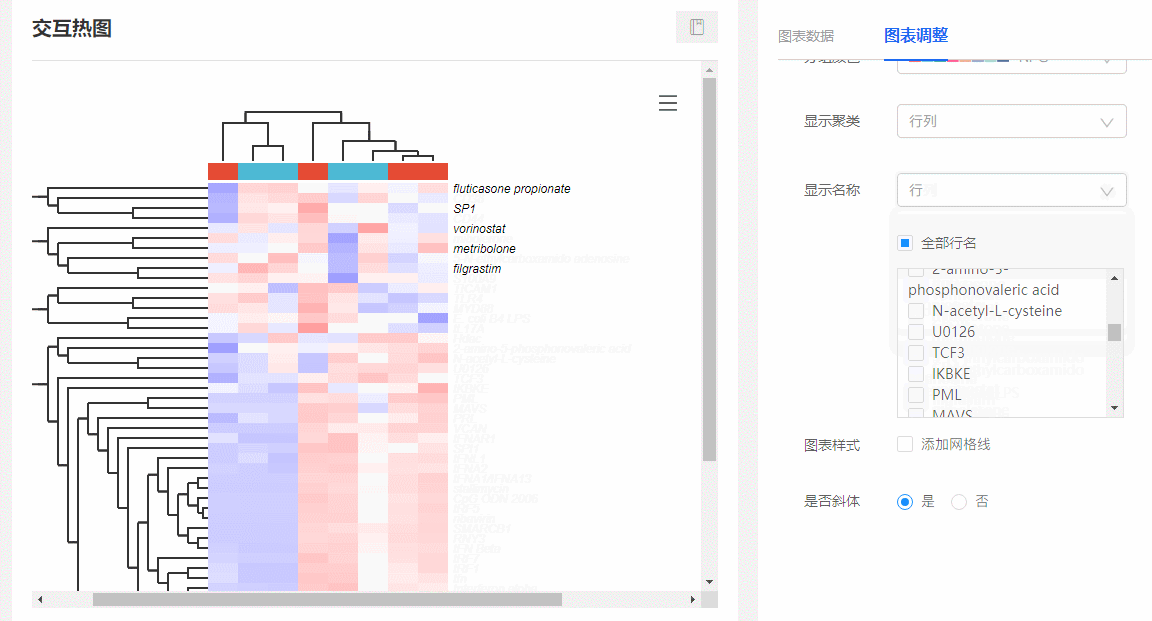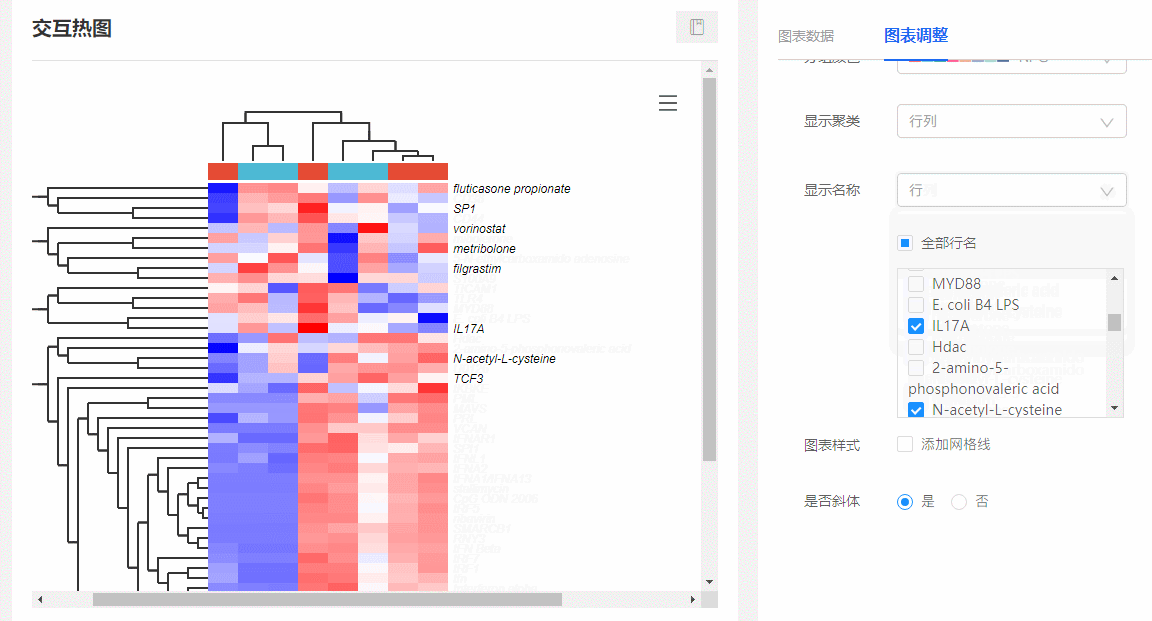
图9 显示特定基因名称
(2)随意伸缩单元格宽高:在图表调整栏,随意拖动【单元格宽度/高度】对应的滑动控制条,可随意更改热图单元格的宽和高。
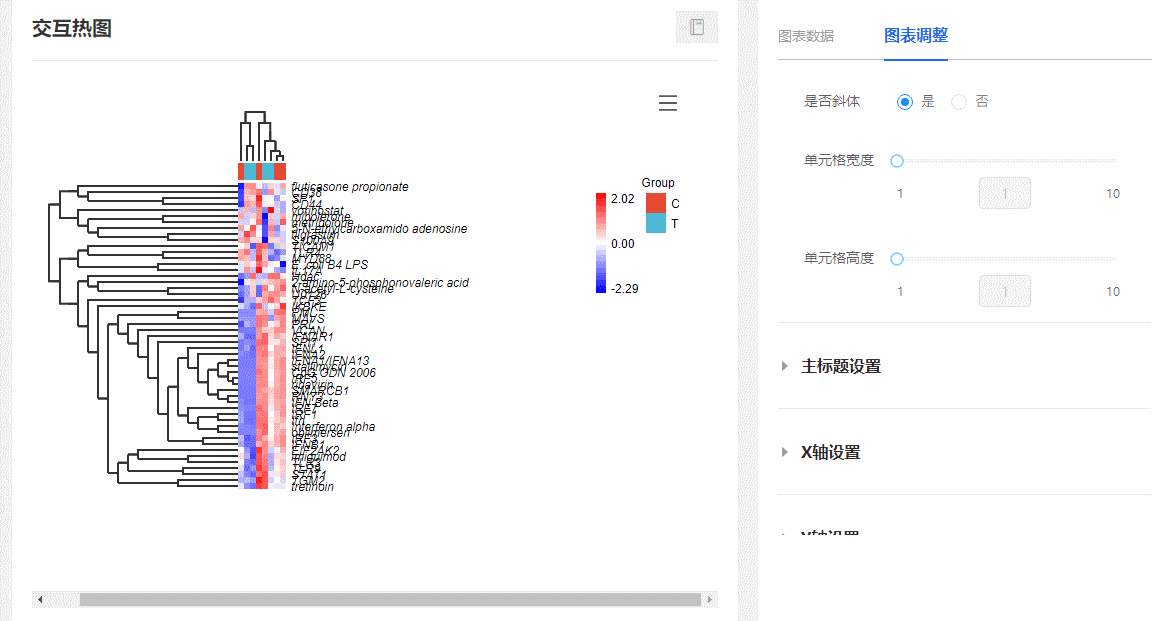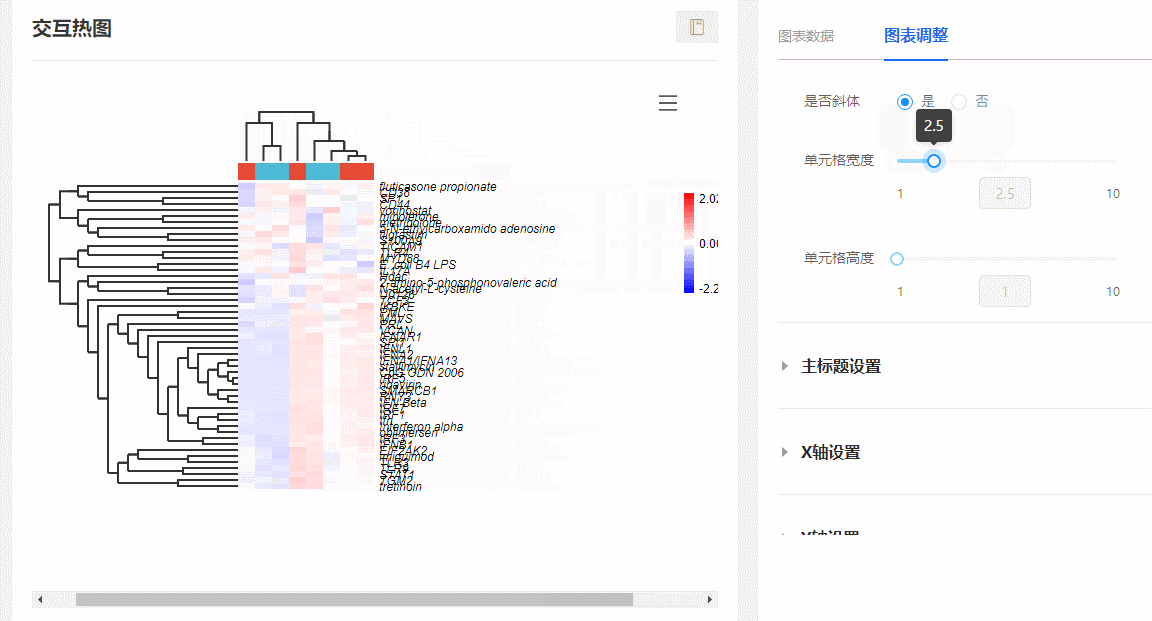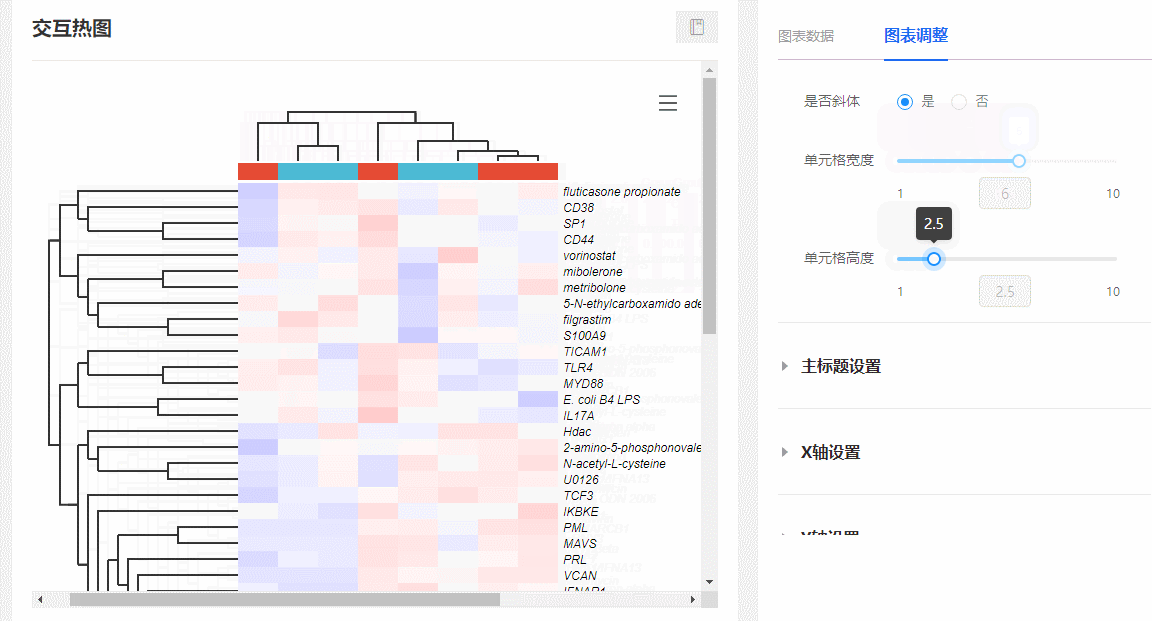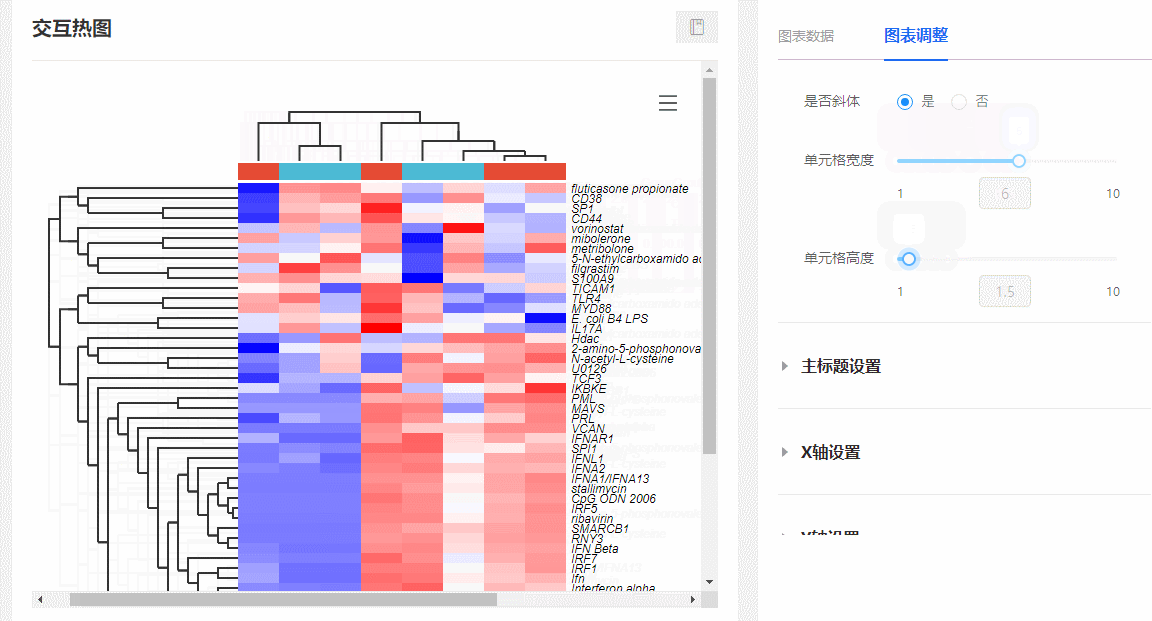
图10 调整单元格长宽
赶紧来试一试吧,百度搜索“派森诺基因云”或者直接访问https://www.genescloud.cn/home,进入“云图汇”搜索“交互热图”尝试体验,并提宝贵建议至平台消息中心-》反馈列表,或者发送到邮箱: gc_support@personalbio.cn。"派森诺基因云" 一直持续上心上新,接下来会有更多好图好工具陆续和大家见面,欢迎大家关注并进行体验。