2023-04-03
GWAS简介
GWAS(Genome-wide Association Studies)是研究动植物复杂性状的重要手段。对于自然群体具有丰富遗传多样性的每个个体进行全基因组重测序,检测分布于全基因组范围的SNP标记,基于连锁不平衡关系,结合不同性状的表型数据,进行分子标记与表型性状的关联分析,可以快速鉴定与目标表型性状变异关联的遗传标记或者候选基因。
GWAS升级后分析流程图
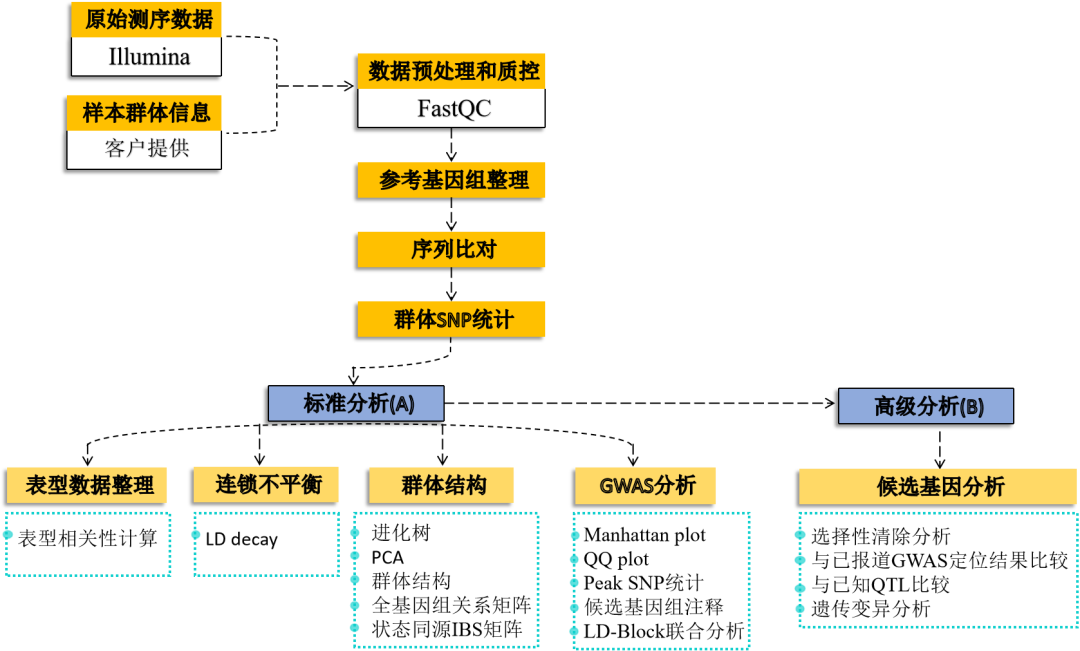
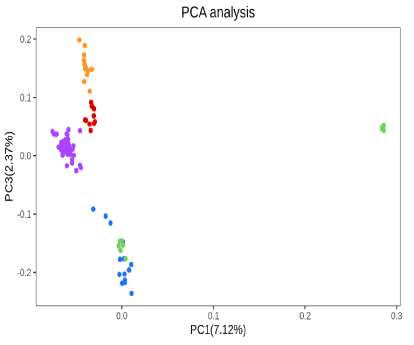
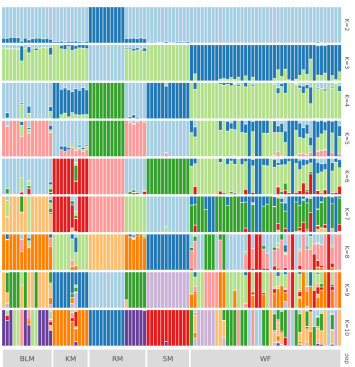
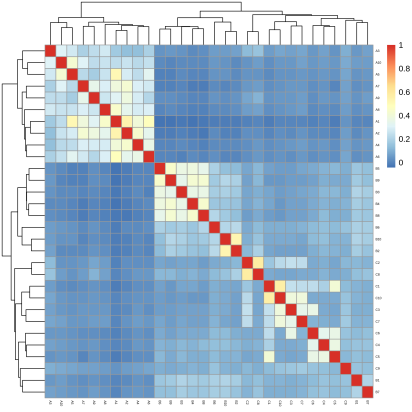
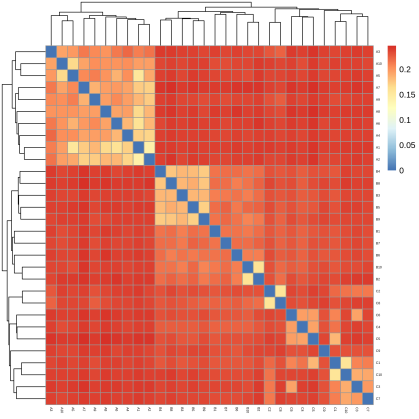
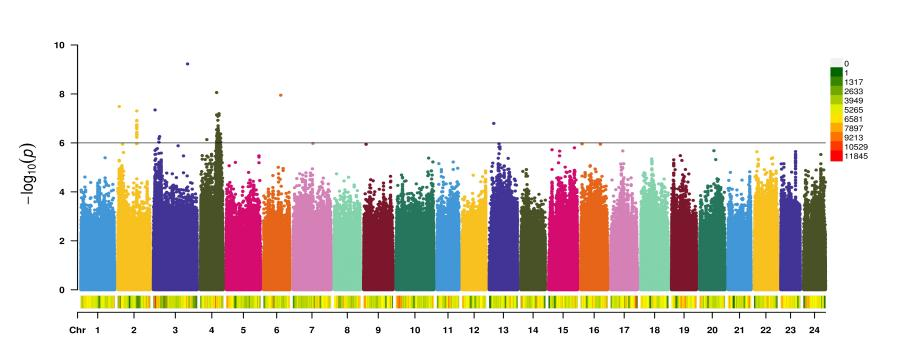
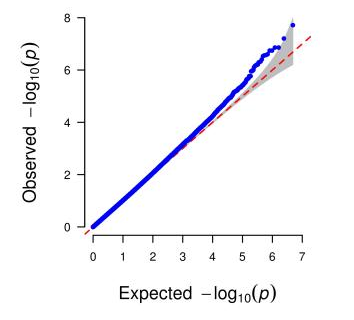
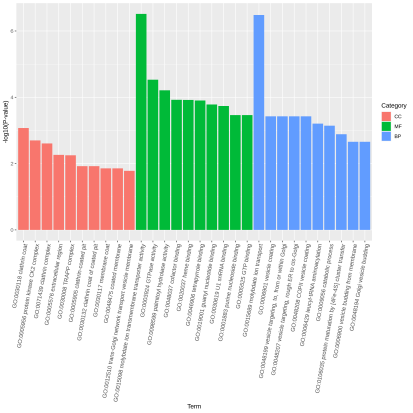
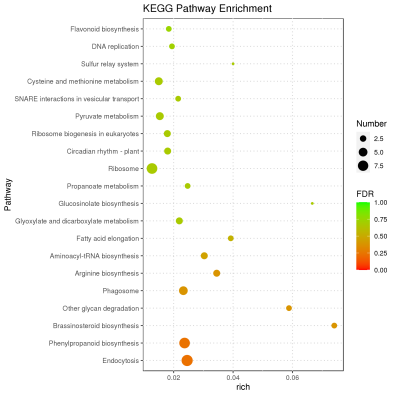
升级亮点一 标准分析多维度挖掘群体遗传多样性信息,丰富文章内容 在产品升级上,派森诺生物一直勤耕不辍。小派结合多年GWAS项目分析经验,对GWAS性状定位产品进行了全新的升级。标准分析在原有的基础上新增加:群体结构分析、全基因组关系矩阵计算、状态同源IBS矩阵计算、LD-Block图绘制,多层次揭示群体遗传进化关系充实文章内容。在定位结果曼哈顿图中增加了SNP在染色体上的分布,不仅在内核上进行升级,在视觉图片上也上升了一个台阶。 序号 分析项目 应用 1 群体结构分析 遗传变异在物种或群体中的分布 2 全基因组关系矩阵Gmatrix 个体间亲缘关系 3 状态同源IBS矩阵 估计个体间共享染色体片段的百分比 4 LD-Block图绘制 单倍型分析 标准分析部分结果展示: 【图】系统进化树 【图】PCA主成分 【图】群体结构 【图】G值矩阵热图 【图】IBS距离矩阵热图 【图】LD分布图 【图】定位结果曼哈顿图 【图】QQ-plot图 【图】LD-Blook图 【图】基因GO富集 【图】基因KEGG富集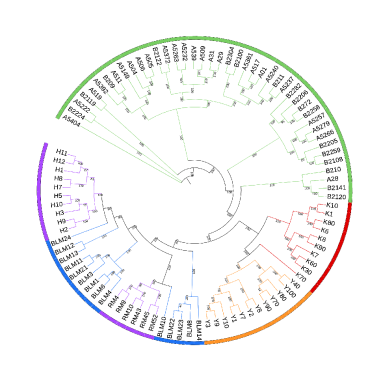
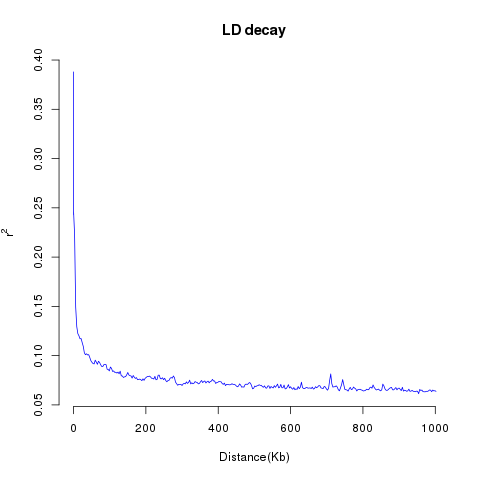
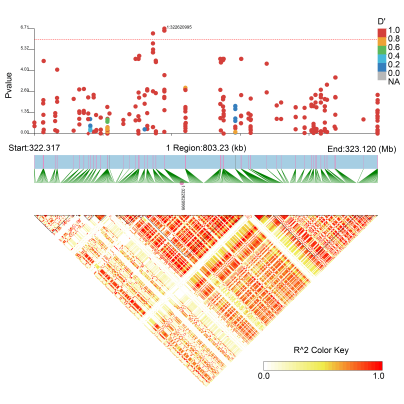
升级亮点二 GWAS定位与LD-Blook图绘制均不限性状个数 在GWAS定位分析后,挖掘到一些显著性SNP位点,如何确定这些位点是不是假阳性呢?我们可以通过可视化snp的LD模式和单倍型块结构的三角相关热图进行判断。由于遗传连锁,附近的单核苷酸多态性(SNPs)通常是高度相关的,或者说位点所在的区域LD值比较高,能形成Block,才比较靠谱。通过LD-Blook联合分析,可以很容易地定位具有最显著关联信号的snp,这对于基因组精细定位研究特别有用。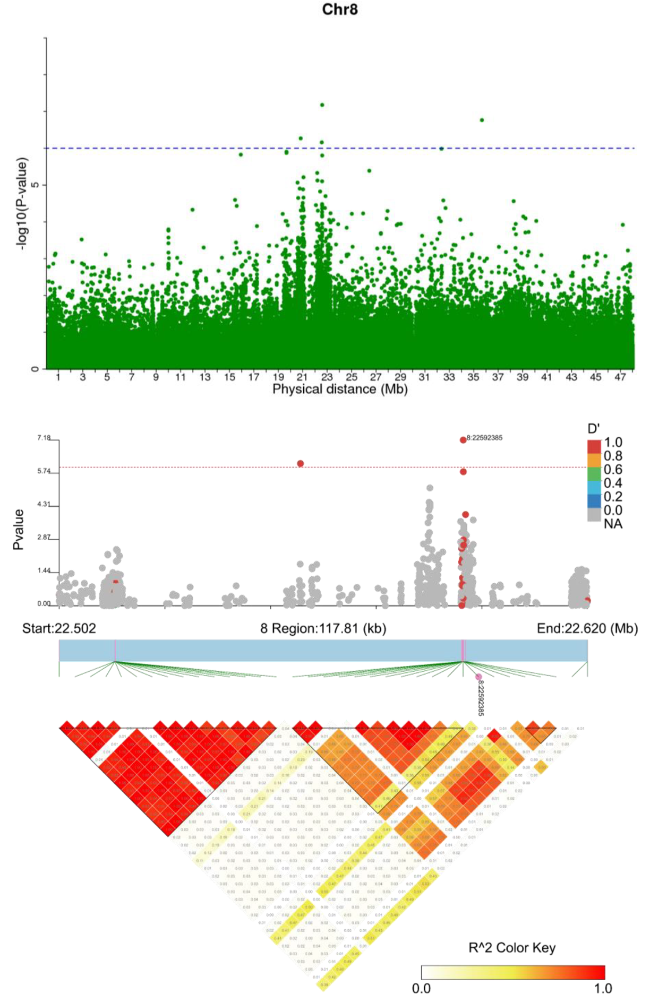
升级亮点三 高级分析——选择性清除分析相互验证 样本量较少找不到GWAS信号,如何巧妙的发文章?小派开展全基因组关联分析,同时利用选择清除分析对不同性状群体受选择区域进行鉴定。1)对于样本较少的项目GWAS定位无信号,可以选择Fst、pi进行选择性清除分析,得到受选择的区域;2)对于GWAS定位效果较好的项目,选择性清除分析与GWAS分析两种分析方法相互印证,提高定位结果准确性。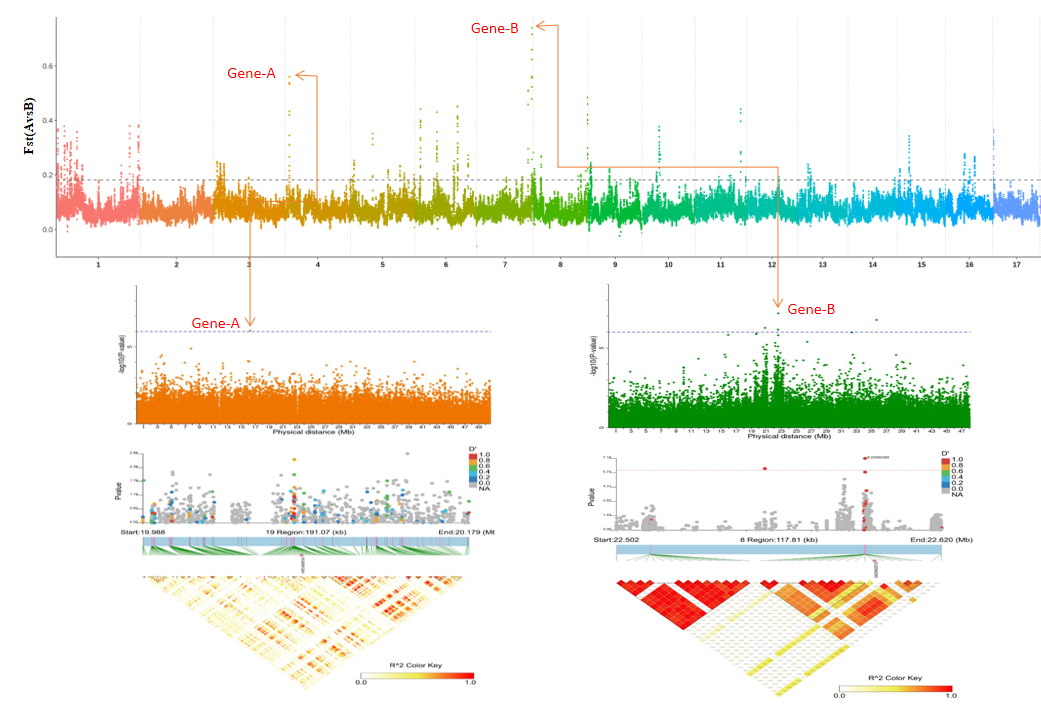
GWAS分析测序策略
选样策略 测序策略 推荐深度 适用范围 1)样本间无明显亚群分化; 2)表型遗传力强; 3)取样具有代表性; 4)样本数不少于200个。 重测序(推荐) ≥5X/样本 有参考基因组 简化测序 基因组≤1G,测1G/样;基因组1G~5G,测2G/样;基因组5G~20G,测5G/样; 参考基因组较大


